在植物生物学知识呈爆炸式增长的当下,每一位研究者都面临着共同的困境:如何从海量、碎片化的专业文献中,快速筛选、提取准确且前沿的核心科学知识?
近日,东北师范大学张铧坤教授团队、英国约翰英纳森中心丁一倞教授团队和英国埃克塞特大学李珂教授团队,在Molecular Plant上发表题为PlantScience.ai: An LLM-Powered Virtual Scientist for Plant Science的研究论文。PlantScience.ai 的横空出世,正是为了破解这一科研痛点,为植物科学研究注入智能新动能。

PlantScience.ai 绝非简单的问答工具,而是一位能持续学习、不断成长的智能科研助手。其核心依托 AutoSKG(自动化科学知识图谱构建)技术,可自动从 CC-BY 授权的开放获取文献中,精准提取基因、蛋白、代谢物等生物实体,以及实体间的关联关系,构建并动态更新庞大的植物科学知识图谱,实现知识的实时迭代。
截至2026年3月,该知识图谱已收录 490万条生物实体、1350万条关联关系,覆盖从模式植物到主要农作物的全领域研究,为科研探索筑牢数据根基。
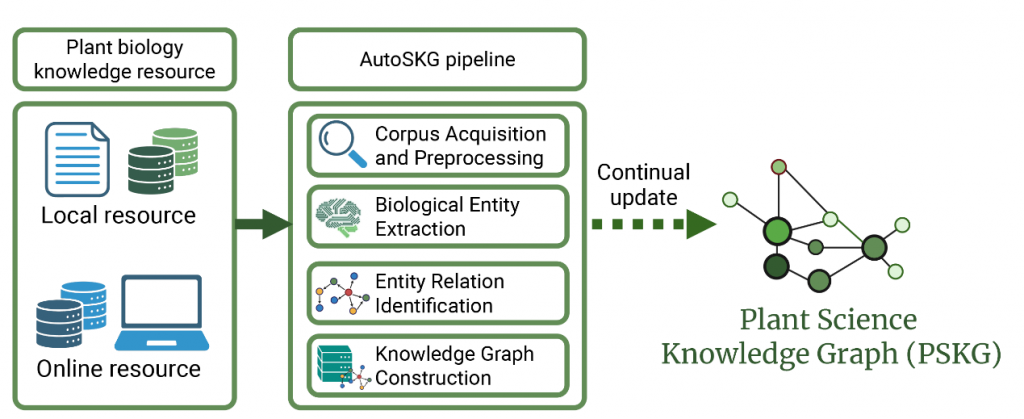
图1. AutoSKG 知识图谱构建流程
区别于通用大语言模型的“泛化短板”,PlantScience.ai 创新引入基于图谱的检索增强生成技术,从根源上解决专业领域“AI幻觉”难题。当用户提出科研问题时,系统将按三步精准响应:
- 精准识别问题中的核心生物实体,锁定研究关键;
- 在动态知识图谱中完成语义搜索与路径遍历,构建完整“知识链”;
- 基于可追溯的原始文献,生成逻辑严谨、内容准确的答案。
每一条回答均附带原始文献的 DOI 链接,用户可一键跳转查看来源,确保信息的真实性与可验证性,让科研引用更放心、更高效。
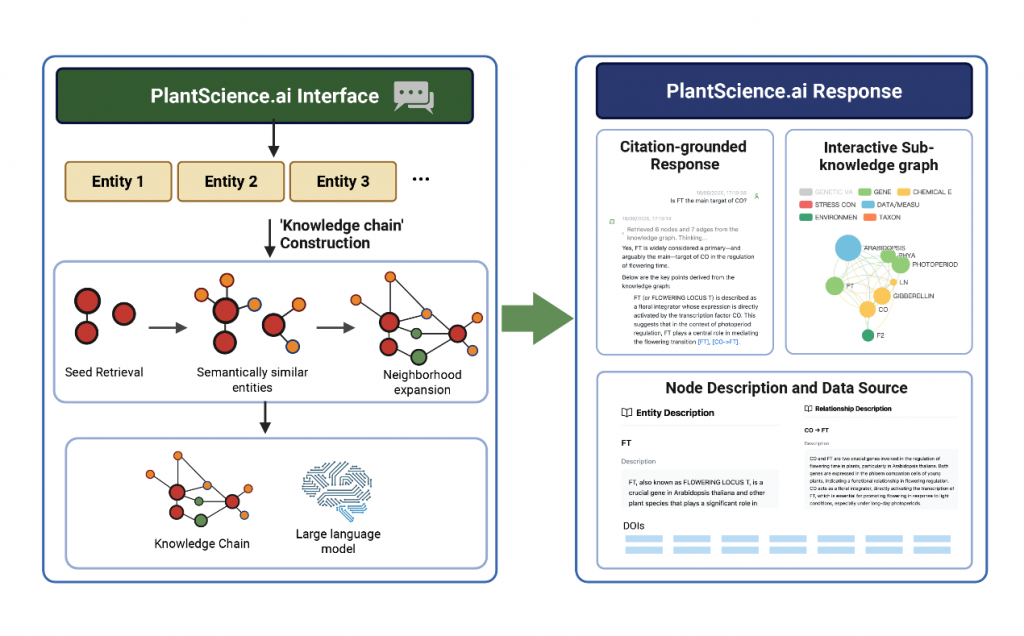
图2. 知识链构建与响应界面
为验证系统性能,研究团队专门构建了涵盖 1770个专业问题、19个植物科学核心类别的评测数据集,邀请54位领域专家与AI评估系统共同开展打分测试。测试结果充分证明了 PlantScience.ai 的专业优势:
- 在事实准确性、内容相关性、信息全面性等核心维度,其表现显著优于 GPT-5、Gemini Pro 等多款主流通用大模型;
- 面对“Bd3-1”“AT1G21130”等专业术语类问题,通用模型几乎全部答错,而 PlantScience.ai 始终能给出精准、详尽的专业解读,彰显领域专属优势。
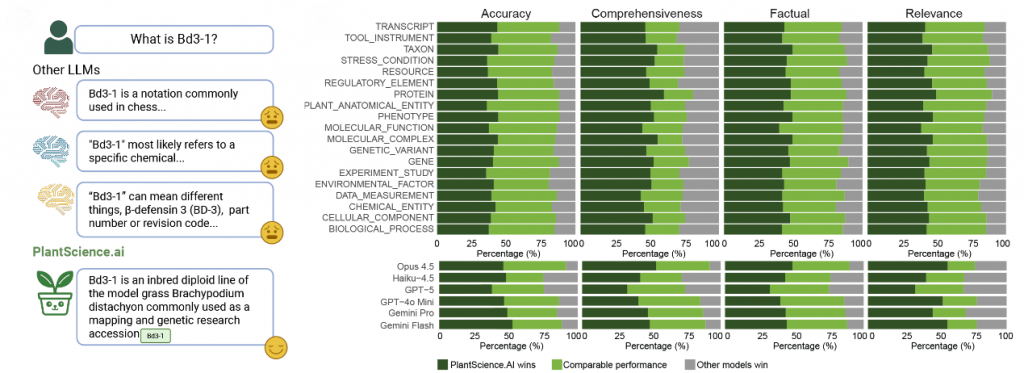
图3. PlantScience.ai 与通用大语言模型的性能对比
PlantScience.ai 不仅聚焦知识提取,其核心架构更为所有面临“信息过载”的学者,提供了可持续学习且个性化的定制:
- 持续学习:依托 AutoSKG 技术,实现知识图谱自动更新,紧跟科研前沿;
- 隐私安全:所有聊天记录仅在客户端本地存储,全程保障用户科研数据隐私;
- 可视化探索:支持交互式知识图谱展示,帮助研究者直观梳理概念关联,挖掘潜在研究方向;
- 开源可定制:AutoSKG 技术已全面开源,用户可基于私有文献,构建专属知识库,适配个性化科研需求。
目前,PlantScience.ai 已面向非商业学术研究免费开放,诚邀全球植物科学研究者共同体验。欢迎访问 https://plantscience.ai 开启智能科研之旅,共推植物科学与人工智能的深度融合,助力科研创新加速落地。
东北师范大学张铧坤教授、英国约翰英纳斯中心丁一倞教授和英国埃克塞特大学李珂教授为共同通讯作者。英国约翰英纳斯中心于昊澎博士、英国埃克塞特大学周莎莎、黄明渝和东北师范大学丁玲并列第一作者。东北师范大学张铧坤教授团队王银茹、任莹钰、程诺、王歆雅、梁杰,英国埃克塞特大学李珂教授团队陈雨轩,联合全体JIC-TSL科学家均为本研究做出贡献。本研究得到以下资助:国家重点研发计划项目、国家自然科学基金项目、中央高校基本科研业务费专项资金、国家留学基金委奖学金、英国生物技术与生物科学研究委员会、欧洲研究理事会、英国皇家学会法拉第发现学者项目、人类前沿科学计划奖学金、研究所发展基金委员会、英国研究与创新署未来领袖学者项目、剑桥唐氏基金会国际学者项目、亚马逊研究奖的支持。